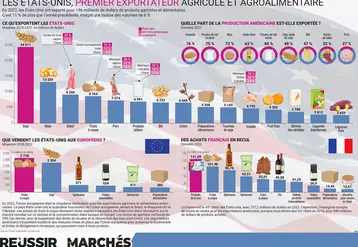
La flore du fromage
La métagénomique un outil analytique puissant
La flore du fromage
Des microbiologistes ont développé un outil capable
de reconnaître la signature génétique de la flore microbienne
des fromages. La méthode permet de dresser la liste
des espèces et leur répartition.

« LE CONCEPT FONCTIONNE
MAIS NOUS DEVONS
COMPLÉTER NOTRE BASE
DE DONNÉES »
©
INRA
MAIS NOUS DEVONS
COMPLÉTER NOTRE BASE
DE DONNÉES »
Identifier le contenu microbien complet d’un fromage est aujourd’hui possible. Dans le cadre du programme de recherche Food Microbiomes, l’Inra de Jouy-en-Josas a mis au point un outil de métagénomique quantitative qui perlyse met de déterminer la liste et la répartition des espèces microbiennes dominantes et sousdominantes présentes dans un fromage.
À PARTIR DE L’ADN
La technique créant l’enthousiasme chez les fromagers, les chercheurs travaillent à simplifier l’outil pour faciliter son transfert. La métagénomique est en effet devenue un moyen analytique plus puissant et moins coûteux qu’autrefois. Son principe est d’identifier les espèces présentes grâce à leurs gènes. L’ana- perlyse débute par l’extraction de l’ADN total de l’échantillon puis le séquençage de ce matériel génétique. Comme certaines séquences sont spécifiques d’une espèce, la méthode consiste à comparer les fragments à une banque de références pour identifier les com perlyse débute par l’extraction de l’ADN total de l’échantillon puis le séquençage de ce matériel génétique. Comme certaines séquences sont spécifiques d’une espèce, la méthode consiste à comparer les fragments à une banque de références pour identifier les communautés présentes. L’approche présente un double avantage : elle permet d’une part d’effectuer une recherche globale plutôt que de cibler une espèce, et d’autre part, de contourner l’écueil de la microbiologie classique qui identifie seulement les micro-organismes cultivables. Ce n’est d’ailleurs pas la première fois que l’Inra tire parti des atouts de cette méthode. « Nous sommes partis d’un outil conçu pour l'étude de la flore intestinale, domaine dans lequel la métagénomique est appliquée depuis plusieurs années, et nous avons transposé l’outil à l’exploration de la flore fromagère », explique Pierre Renault, directeur de recherche et coordonnateur du programme Food Microbiomes.
QUANTITÉS D’APPLICATIONS POSSIBLES
Conduits en collaboration avec le Cniel, les travaux ont commencé par la collecte de 150 espèces de bactéries et 21 espèces de levures et champignons, auprès des fromagers et des centres de recherche. Ces espèces ont été utilisées pour créer une banque de références. Grâce à celle-ci, les chercheurs peuvent aujourd’hui retrouver, par comparaison, la signature des différentes communautés présentes dans un fromage, quelles qu’elles soient. La méthode apparaît robuste.
« Pour prouver la cohérence des résultats, nous avons divisé un fromage en deux portions : notre outil recense bien les mêmes espèces dans la portion 1 et la portion 2 », explique Pierre Renault, directeur de recherche et coordonnateur du programme. Assez sensible pour identifier les espèces dominantes comme sous-dominantes dans un rapport de 1 contre 100000, la méthode permet de recenser les flores présentes à la surface, à coeur ou dans le fromage entier. Les chercheurs évoquent plusieurs applications possibles pour l’industrie. « Par exemple, notre outil peut comparer l’évolution des communautés selon différents procédés ou différentes recettes, et aider à comprendre comment la qualité ou la non qualité d’un fromage se construit », explique Pierre Renault. Capable de reconnaître la signature génétique des différentes souches, la méthode permet aussi de vérifier que les souches ajoutées au lait pendant la fabrication sont bien celles retrouvées dans le fromage à la fin de la fabrication.
DANS LES ENTREPRISES D’ICI 4 À 5 ANS
Actuellement, les chercheurs s’emploient à faciliter le transfert de cette méthodologie vers Actilait et vers les entreprises pour lesquelles le coût ne devrait plus être un frein. Le coût des appareils va continuer de baisser. Ceci devrait permettre aux industriels de s’équiper. Mais le matériel n’est pas tout : les entreprises devront aussi s’entourer de collaborateurs compétents. Il faudra vraisemblablement encore 4 à 5 ans pour qu’elles s’approprient la méthode.
Rédaction Réussir
À PARTIR DE L’ADN
La technique créant l’enthousiasme chez les fromagers, les chercheurs travaillent à simplifier l’outil pour faciliter son transfert. La métagénomique est en effet devenue un moyen analytique plus puissant et moins coûteux qu’autrefois. Son principe est d’identifier les espèces présentes grâce à leurs gènes. L’ana- perlyse débute par l’extraction de l’ADN total de l’échantillon puis le séquençage de ce matériel génétique. Comme certaines séquences sont spécifiques d’une espèce, la méthode consiste à comparer les fragments à une banque de références pour identifier les com perlyse débute par l’extraction de l’ADN total de l’échantillon puis le séquençage de ce matériel génétique. Comme certaines séquences sont spécifiques d’une espèce, la méthode consiste à comparer les fragments à une banque de références pour identifier les communautés présentes. L’approche présente un double avantage : elle permet d’une part d’effectuer une recherche globale plutôt que de cibler une espèce, et d’autre part, de contourner l’écueil de la microbiologie classique qui identifie seulement les micro-organismes cultivables. Ce n’est d’ailleurs pas la première fois que l’Inra tire parti des atouts de cette méthode. « Nous sommes partis d’un outil conçu pour l'étude de la flore intestinale, domaine dans lequel la métagénomique est appliquée depuis plusieurs années, et nous avons transposé l’outil à l’exploration de la flore fromagère », explique Pierre Renault, directeur de recherche et coordonnateur du programme Food Microbiomes.
QUANTITÉS D’APPLICATIONS POSSIBLES
Conduits en collaboration avec le Cniel, les travaux ont commencé par la collecte de 150 espèces de bactéries et 21 espèces de levures et champignons, auprès des fromagers et des centres de recherche. Ces espèces ont été utilisées pour créer une banque de références. Grâce à celle-ci, les chercheurs peuvent aujourd’hui retrouver, par comparaison, la signature des différentes communautés présentes dans un fromage, quelles qu’elles soient. La méthode apparaît robuste.
« Pour prouver la cohérence des résultats, nous avons divisé un fromage en deux portions : notre outil recense bien les mêmes espèces dans la portion 1 et la portion 2 », explique Pierre Renault, directeur de recherche et coordonnateur du programme. Assez sensible pour identifier les espèces dominantes comme sous-dominantes dans un rapport de 1 contre 100000, la méthode permet de recenser les flores présentes à la surface, à coeur ou dans le fromage entier. Les chercheurs évoquent plusieurs applications possibles pour l’industrie. « Par exemple, notre outil peut comparer l’évolution des communautés selon différents procédés ou différentes recettes, et aider à comprendre comment la qualité ou la non qualité d’un fromage se construit », explique Pierre Renault. Capable de reconnaître la signature génétique des différentes souches, la méthode permet aussi de vérifier que les souches ajoutées au lait pendant la fabrication sont bien celles retrouvées dans le fromage à la fin de la fabrication.
DANS LES ENTREPRISES D’ICI 4 À 5 ANS
Actuellement, les chercheurs s’emploient à faciliter le transfert de cette méthodologie vers Actilait et vers les entreprises pour lesquelles le coût ne devrait plus être un frein. Le coût des appareils va continuer de baisser. Ceci devrait permettre aux industriels de s’équiper. Mais le matériel n’est pas tout : les entreprises devront aussi s’entourer de collaborateurs compétents. Il faudra vraisemblablement encore 4 à 5 ans pour qu’elles s’approprient la méthode.